准备工作
Git
Git是一款免费、开源的分布式版本控制系统,用于敏捷高效地处理任何或小或大的项目。 Git是用于Linux内核开发的版本控制工具。可以在Windows电脑上利用Linux命令处理文件。
Rstudio中配置Git
工作台中存在Teminal栏,说明Git已经配置完成。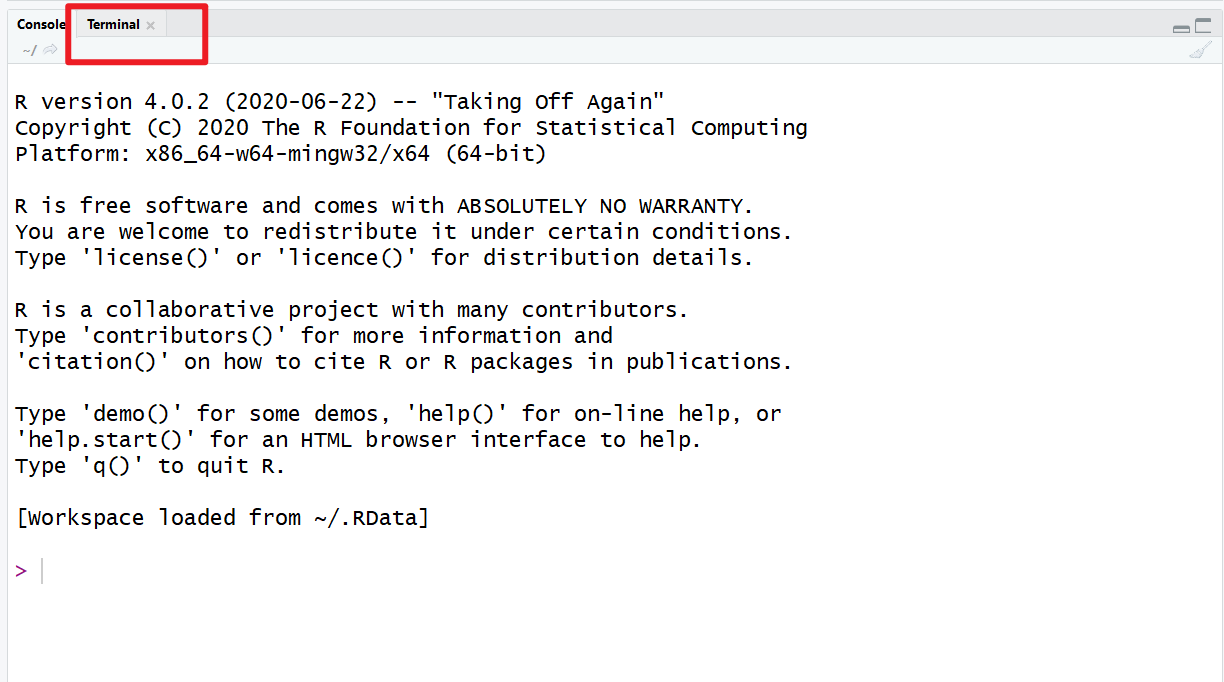
若无Terminal栏,则按以下步骤配置。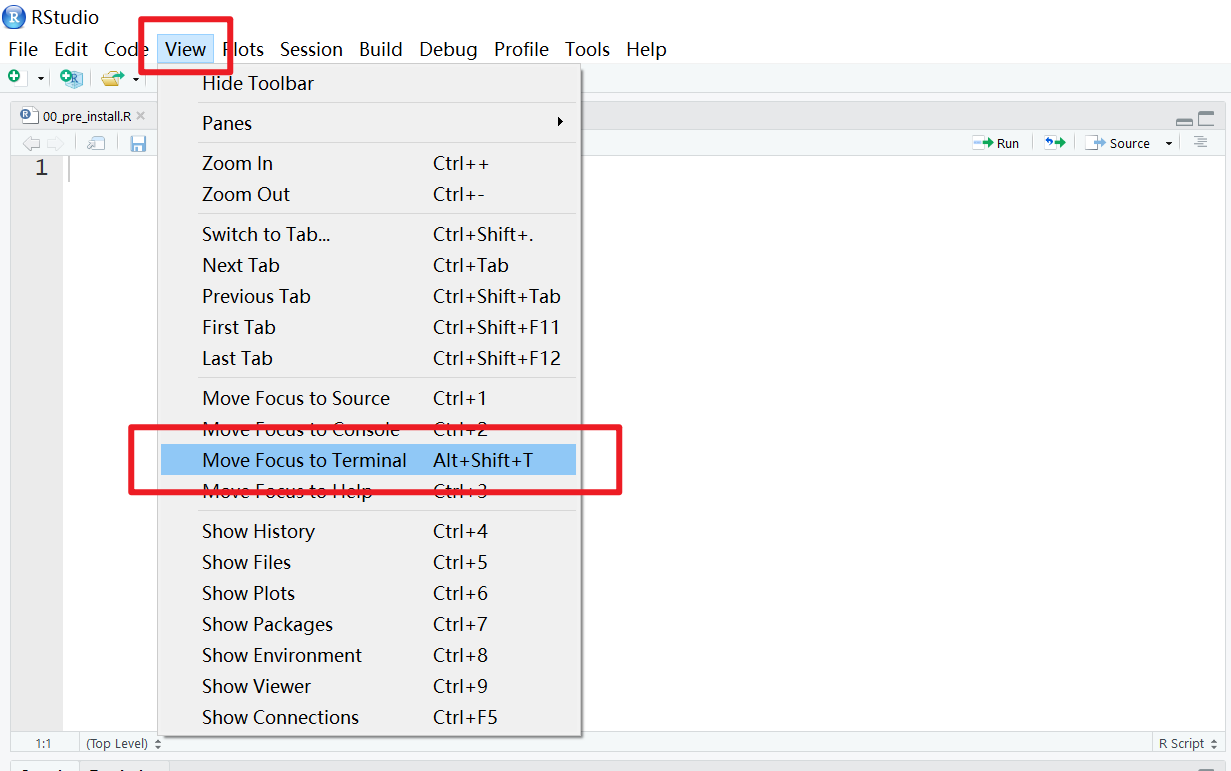

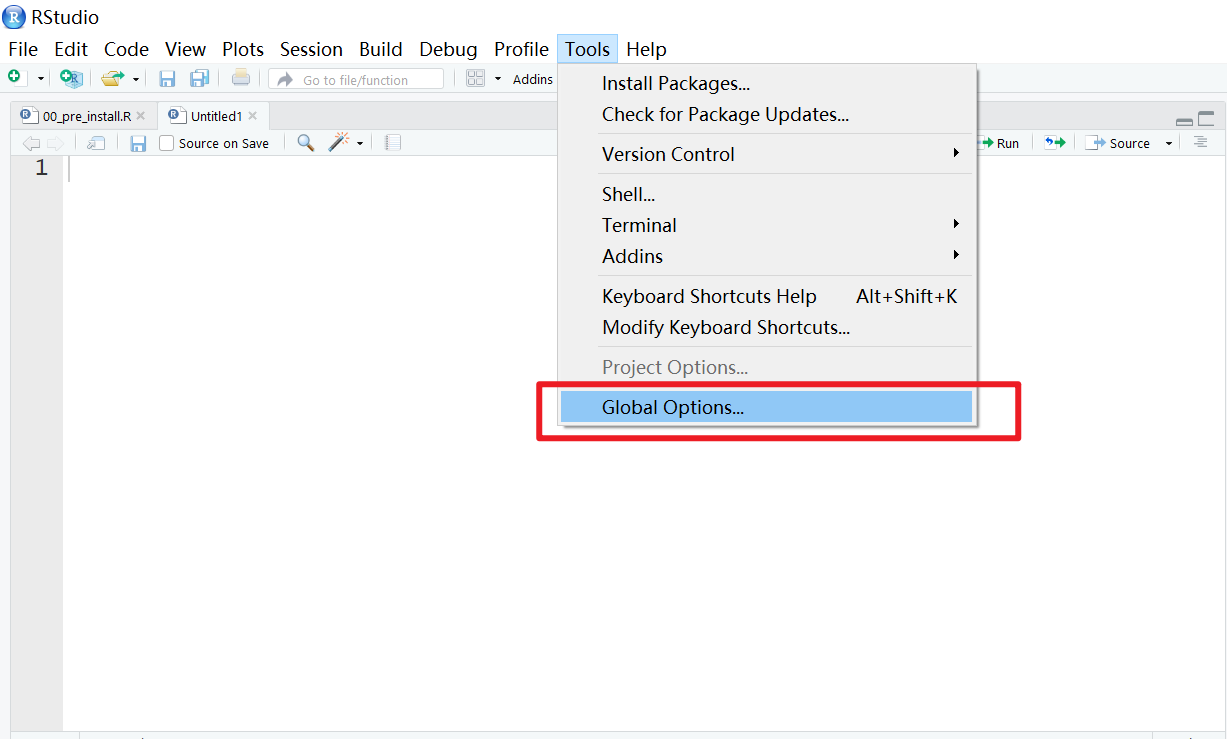
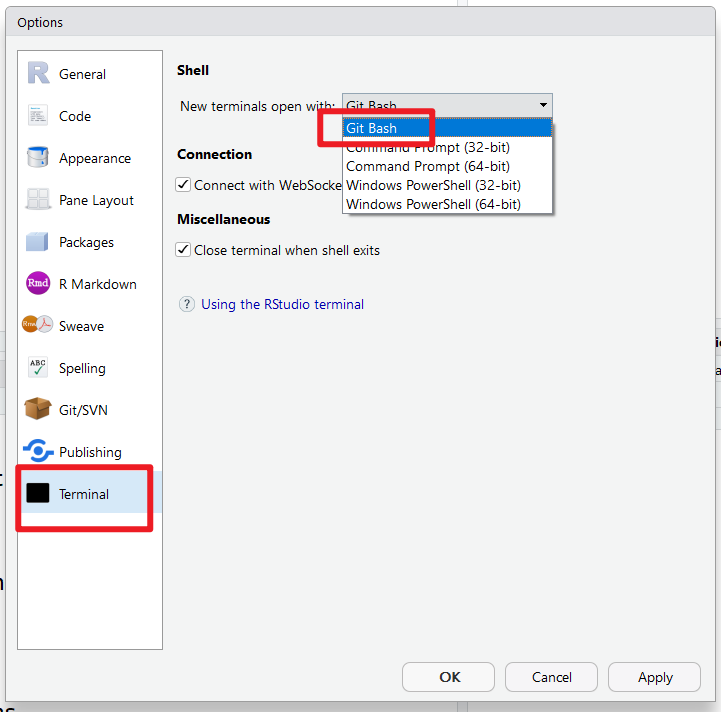
Rmd
Markdown是一种简单的文本文件格式, 通常保存为.md扩展名。 Mardown中文内容应该使用UTF-8编码。 Markdown文件里面有一些简单的格式标注方法, 比如两个星号之间的文字会转化为粗体。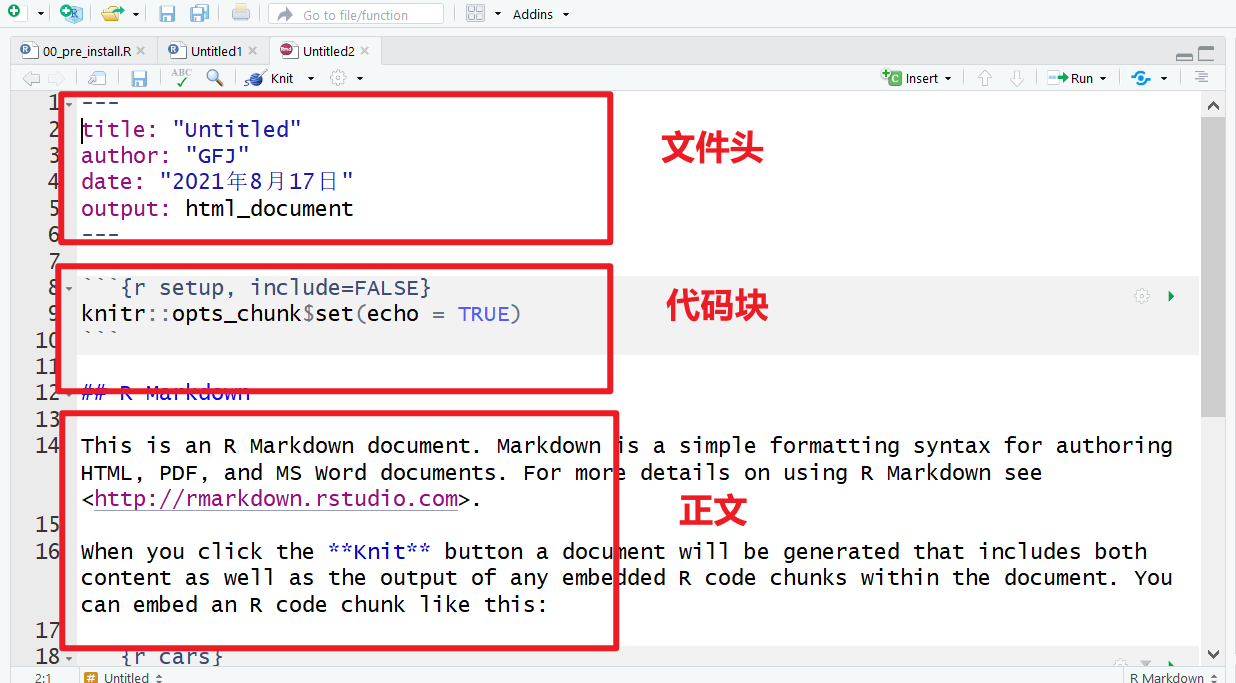
插入代码块
## 两种方法
ctrl+alt+i
<a name="x8pCr"></a>### 运行代码<a name="vJcDB"></a>### markdown基本语法```r# ## 级别标题``` ## 行内代码** ** ## 中间文本加粗> ## 引用
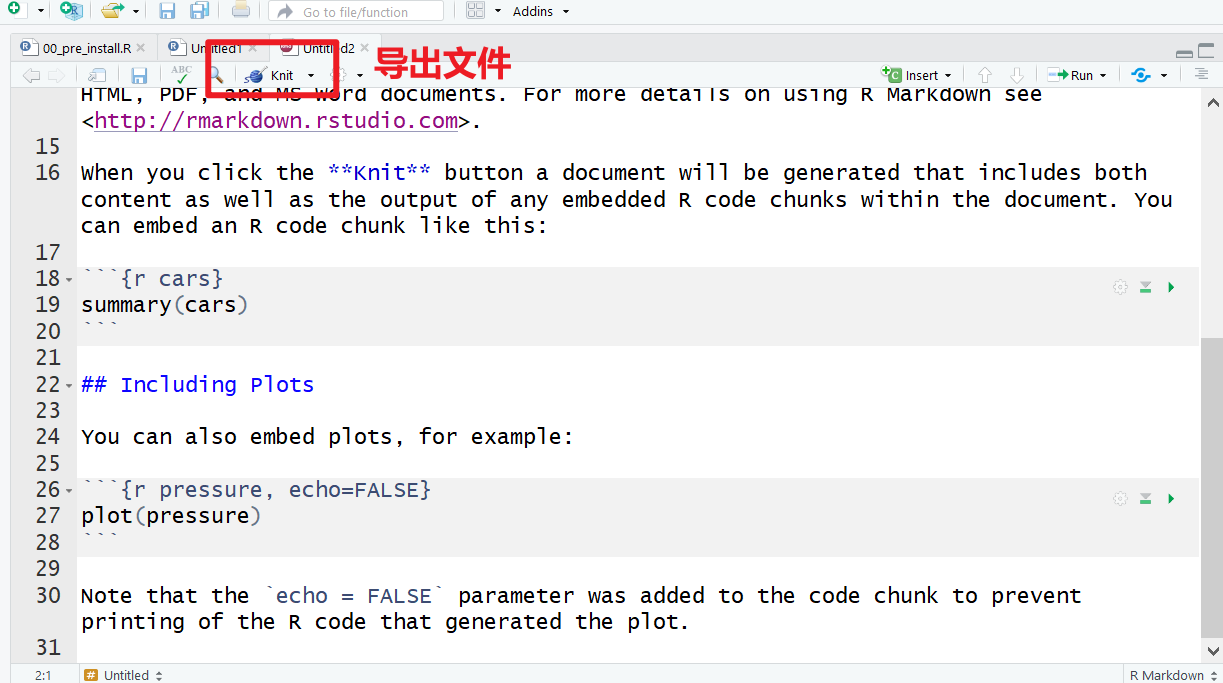
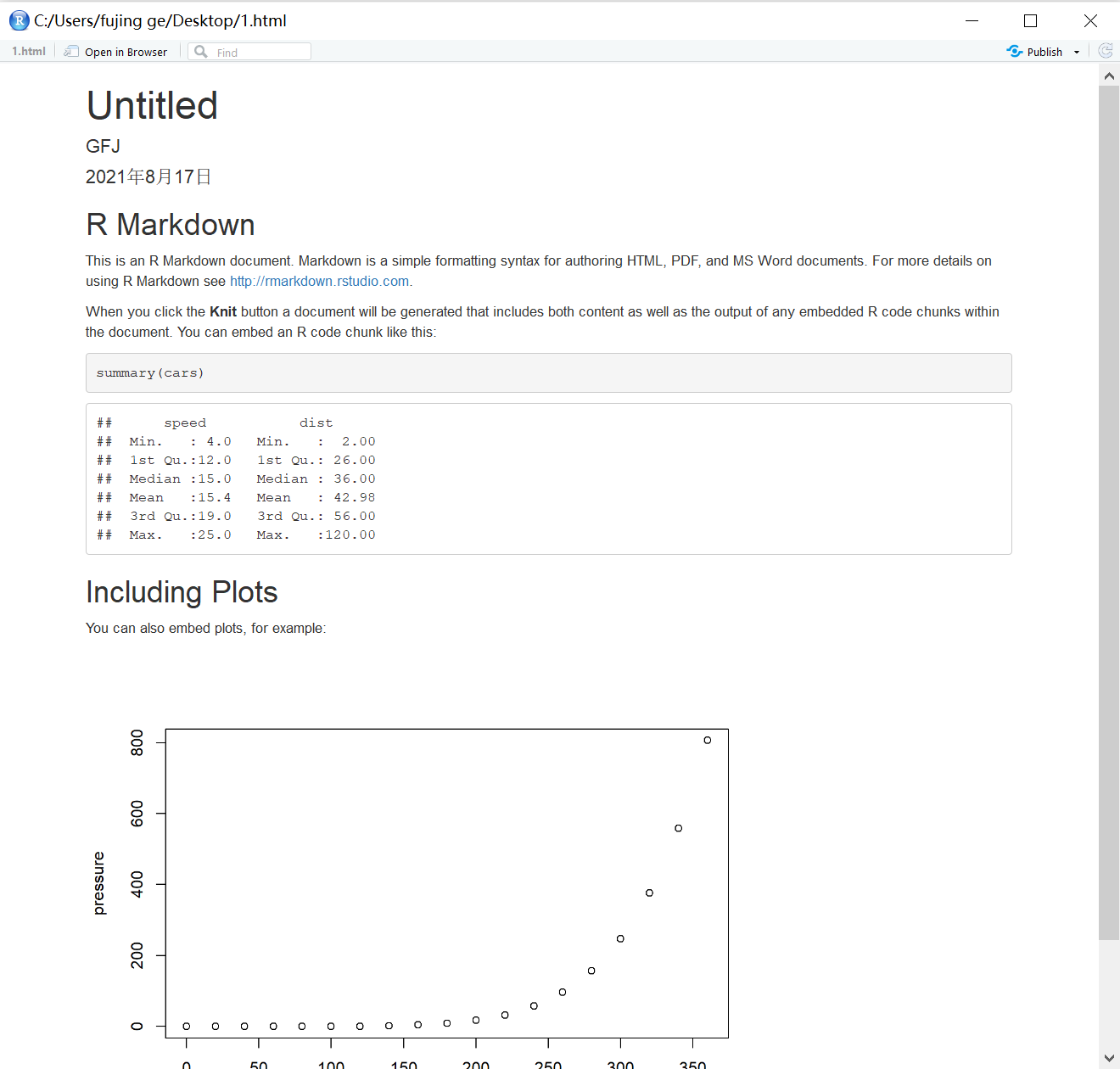
渲染导出文件
TCGA数据库
TCGA全称The Cancer Genome Atlas。是由National Cancer Institute ( NCI, 美国国家癌症研究所) 和 National Human Genome Research Institute (NHGRI, 国家人类基因组研究所) 合作建立的癌症研究项目,通过收集整理癌症相关的各种组学数据,提供了一个大型的,免费的癌症研究参考数据库。
目前共收录了33种癌症类型,超过了2个PB的数据,该数据是免费公开的,极大的帮助癌症研究者提高对癌症的预防,诊断和治疗。该数据库的网址如下
https://www.cancer.gov/about-nci/organization/ccg/research/structural-genomics/tcga
数据类型包括以下几种
- RNA sequencing
- MicroRNA sequencing
- DNA sequencing
- SNP-based platforms
- Array-based DNA methylation sequencing
- Reverse-phase array(RPPA)
涵盖了基因组,转录组,表观遗传,蛋白组等各个组学数据,提供了一个全方位,多维度的数据。 官方提供了对应的下载工具Genomic Data Commons Datga Portal, 简称GDC, 网址如下
https://portal.gdc.cancer.gov/
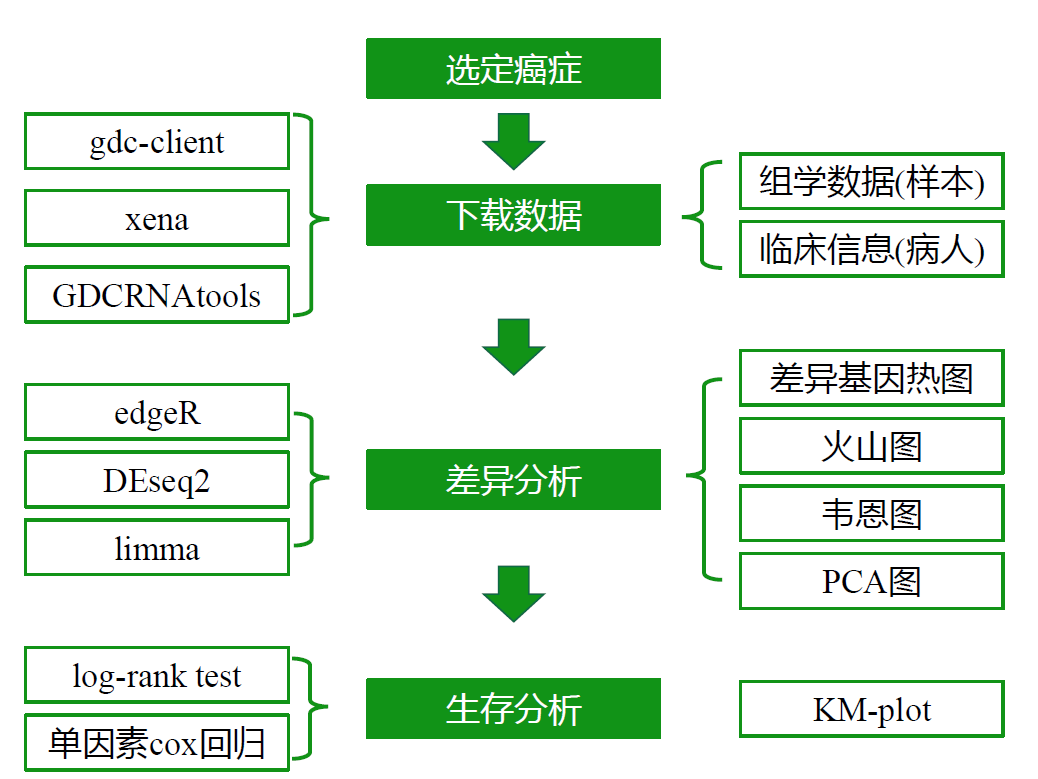
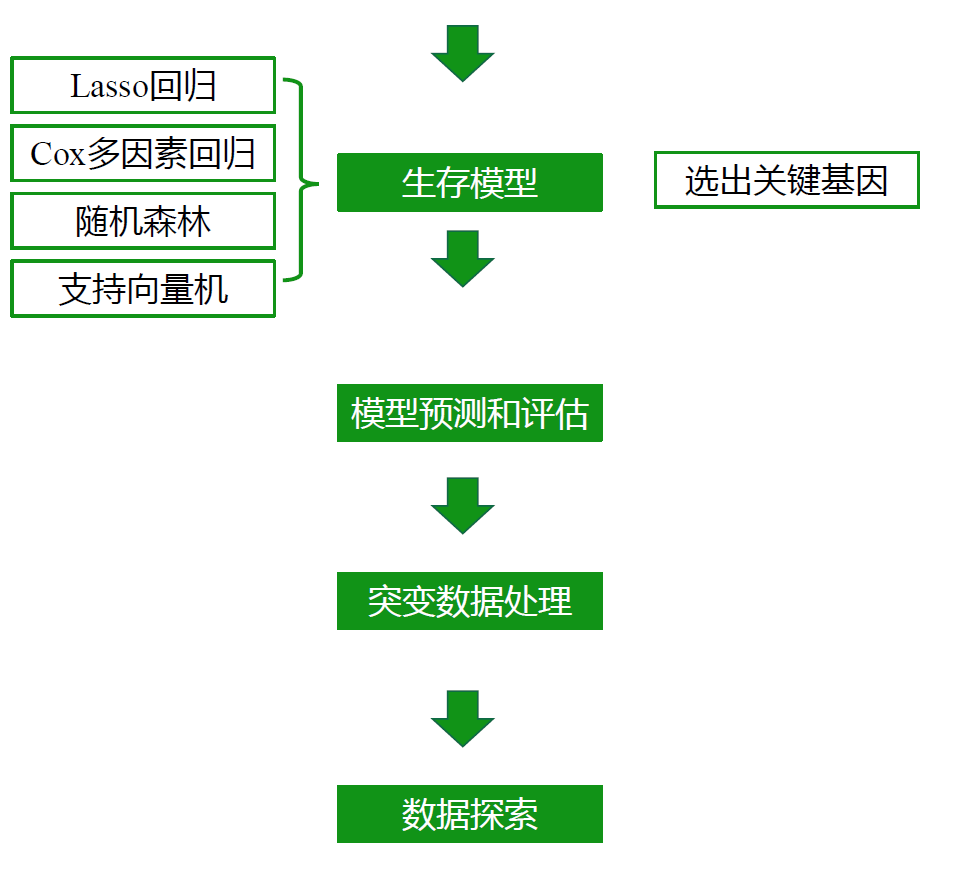
TCGA数据分流程