目前空间转录组拟时序分析工具主要有:
stLearn
SPATA
其他应用于单细胞发育轨迹分析的算法(monocle3,RNA velocity等)
本期主要介绍stLearn[1]。
单细胞的发育轨迹算法
先回顾一下应用于单细胞的发育轨迹算法。
常用的方法有以下几种:
目前已发表的发育轨迹算法很多,超过70种[2]。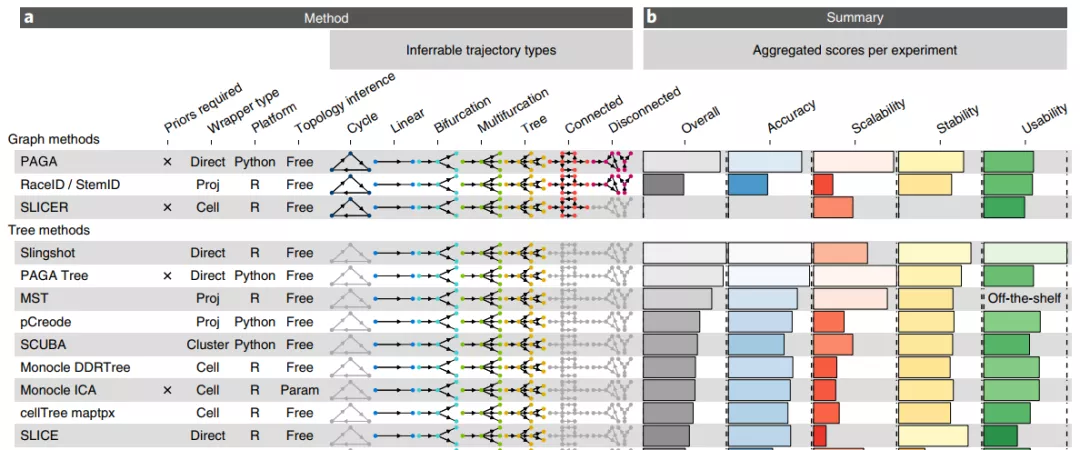
鉴于选择困难症,R包dyno提供了友好的交互界面。用户可以根据自己的数据特征和研究目的,选择合适的拟时序方法[3]。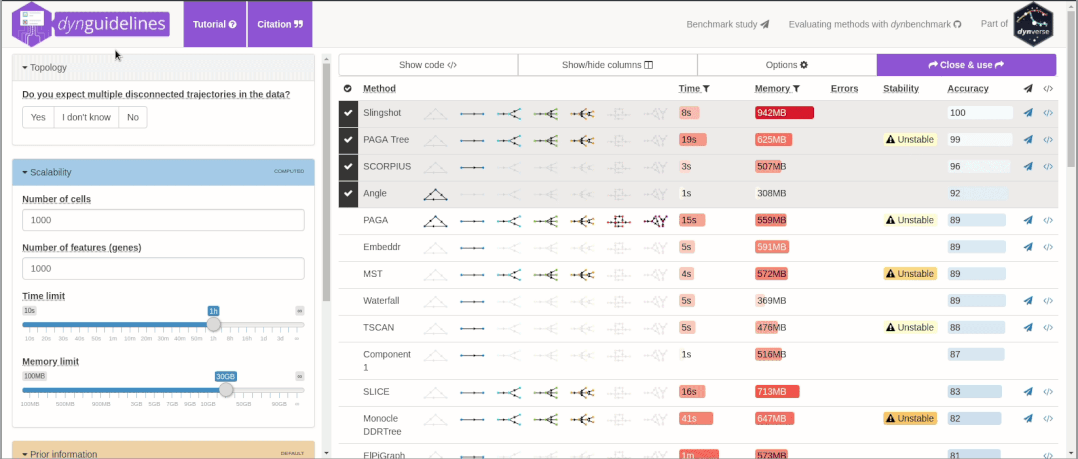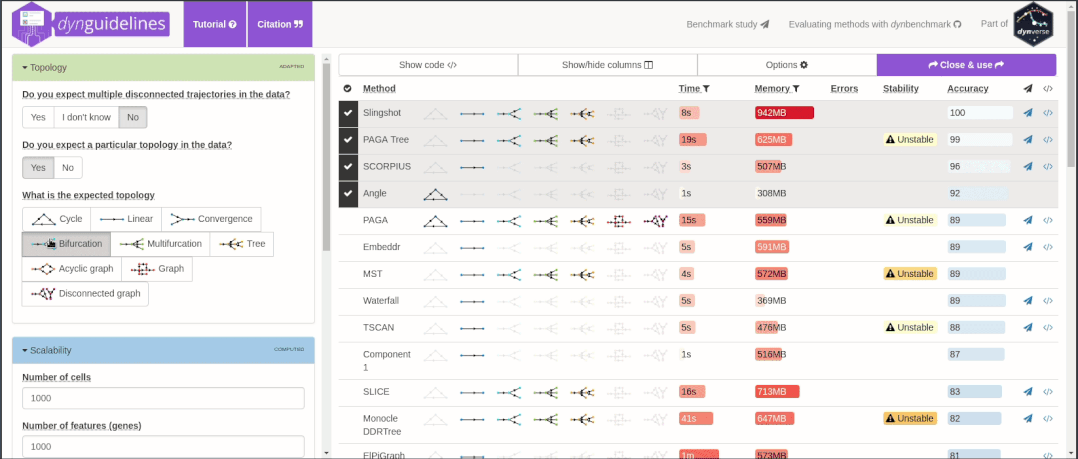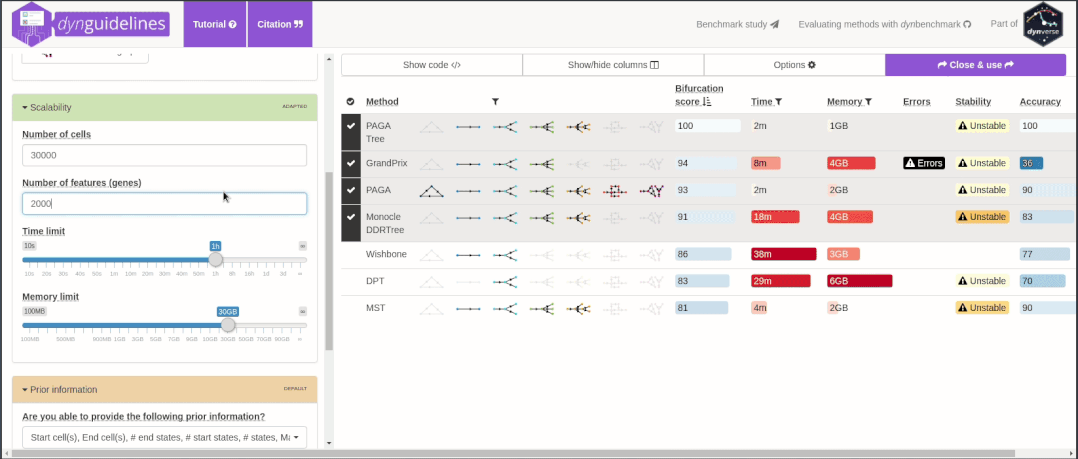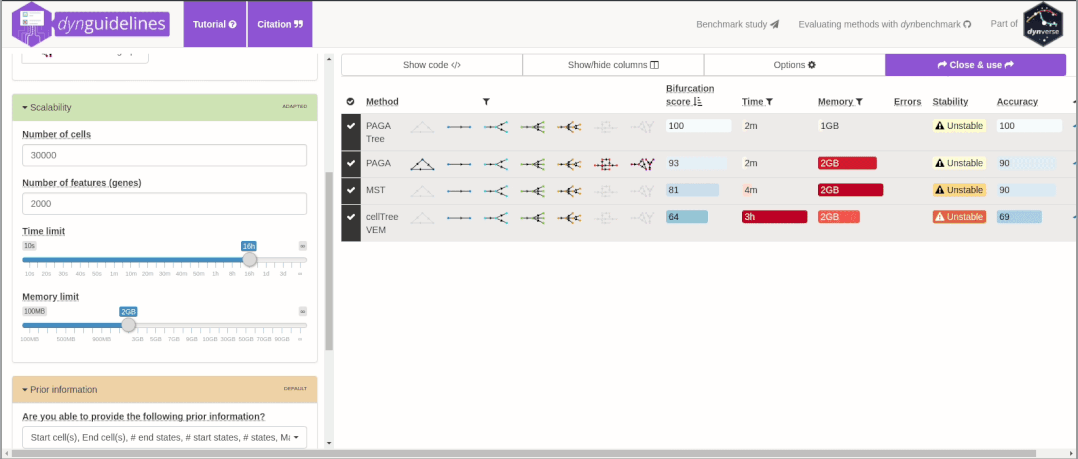
回到空间转录组。以10X visium的乳腺癌数据为例,stLearn的拟时序分析结果可以展示细胞在切片上的侵袭轨迹,从粉红色区域的导管癌细胞,到蓝色区域的侵袭性导管癌细胞。
stLearn拟时序算法原理
stLearn的拟时序算法主要基于DPT,结合空间坐标信息,调整spot之间的拟时序距离,最后用最小生成树,简化得到发育轨迹。具体步骤:
- 确定起始点;
- 计算DPT距离;
- 结合空间位置,计算PSTD距离;
- 构建方向树;
- 用最小生成树算法精简分支(最小权重连接所有节点,类似第一代monocle)
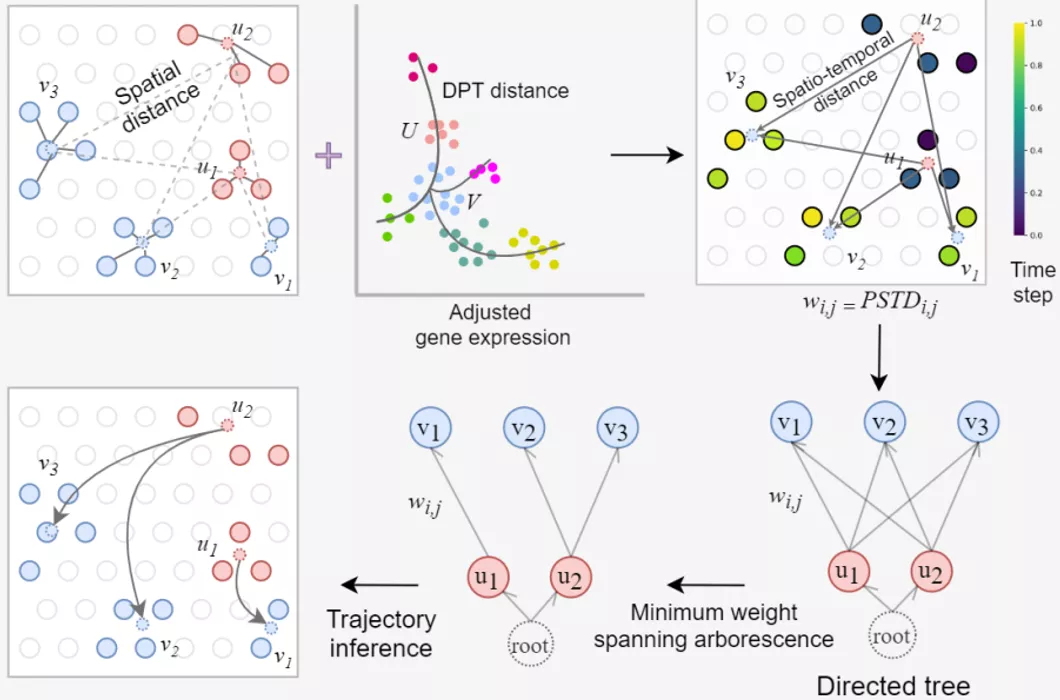
算法细节:PSTD距离的计算。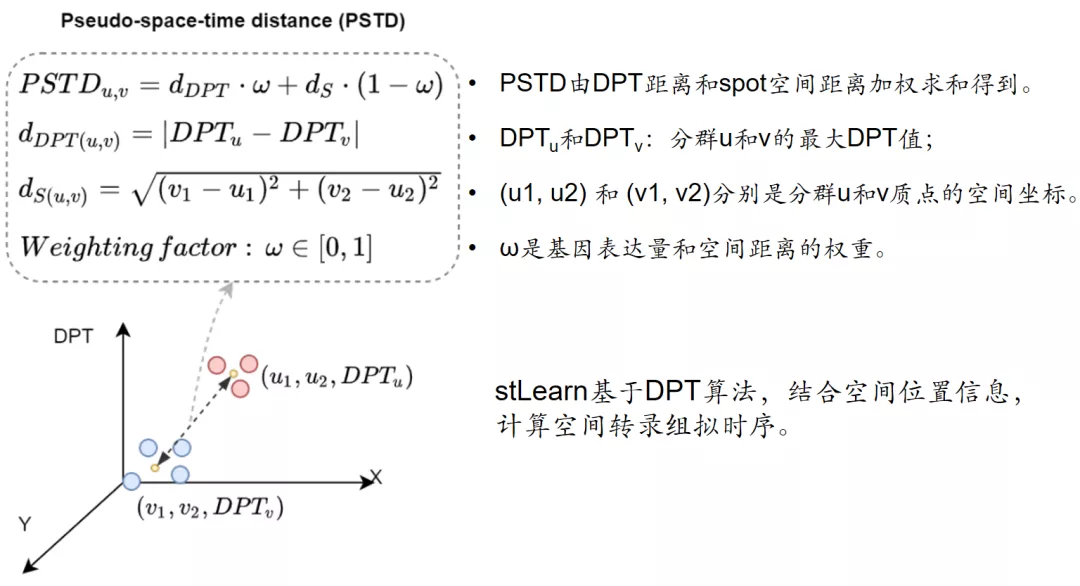
可以看出,stLearn算法主要特点,是DPT距离和切片上的二维欧氏距离的结合。
缺点
结果受起始位点的选择和细胞类型注释的影响较大。
下期预告:RNA velocity,衍生的多组学velocity,以及其中的系统生物学原理。
参考链接:
[1] Pham D T, Tan X, Xu J, et al. stLearn:integrating spatial location, tissue morphology and gene expression to findcell types, cell-cell interactions and spatial trajectories within undissociatedtissues[J]. bioRxiv,2020.
[2] Saelens W, Cannoodt R, Todorov H, et al. A comparison of single-cell trajectory inference methods[J]. Nature biotechnology, 2019, 37(5): 547-554.
[3] https://github.com/dynverse/dyno

